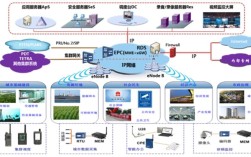
gff技术和ogs技术是基因组学研究中两种重要的技术手段,分别在基因结构注释和功能基因组学分析中发挥着关键作用,gff(通用格式特征文件)技术是一种标准化的文件格式规范,用于描述基因组序列中的各种特征信息,如基因、外显子、内含子、启动子、调控元件等,该技术由序列特征表(Sequence Ontology,SO)项目维护,采用分层结构定义特征类型,通过九个字段(seqid、source、type、start、end、score、strand、phase、attributes)对基因组特征进行精确描述,在人类基因组参考序列中,gff3文件可以通过"ID=gene:ENSG000001396;Name=BRCA1"等属性明确标识每个基因的唯一标识符和名称,便于后续的生物信息学分析和可视化,gff技术的优势在于其通用性和可扩展性,支持不同基因组注释工具之间的数据交换,如Ensembl、NCBI等数据库均采用该格式存储基因注释结果。
ogs(直系同源基因簇)技术则是基于系统发育关系和序列相似性,将不同物种中起源于共同祖先的基因进行聚类分析的方法,该技术通过构建多序列比对和系统发育树,识别直系同源基因(orthologs)和旁系同源基因(paralogs),为跨物种功能比较和进化研究提供基础,ogs分析通常包含以下步骤:使用BLAST或DIAMOND等工具进行全基因组范围的序列比对;通过OrthoMCL、InParanoid等软件聚类算法识别同源基因簇;结合功能注释和表达数据验证同源基因的功能保守性,在比较人类和小鼠基因组时,ogs技术可识别出约18000对直系同源基因,这些基因在功能上高度保守,是研究疾病模型和药物靶点的重要依据。
两种技术的结合应用为基因组学研究提供了强大支持,通过ogs技术识别的直系同源基因簇,可以利用gff文件中的基因结构信息进行跨物种外显子-内含子结构比较,揭示基因进化的分子机制,在植物基因组研究中,ogs技术常用于分析作物野生近缘种的直系同源基因,结合gff注释的顺式作用元件信息,可挖掘与抗逆性相关的关键基因,在宏基因组学研究中,ogs技术可用于环境样本中功能基因的分类,而gff格式则能帮助定位这些基因在宏基因组组装contig上的位置。
以下是两种技术的应用对比:
| 比较维度 | gff技术 | ogs技术 |
|---|---|---|
| 主要功能 | 基因组特征结构标注 | 同源基因聚类与进化分析 |
| 数据类型 | 基因位置、结构、属性 | 序列相似性、系统发育关系 |
| 分析工具 | AGAT、BEDTools | OrthoFinder、eggNOG |
| 应用场景 | 基因注释可视化、变异检测 | 跨物种功能比较、进化树构建 |
相关问答FAQs:
-
问:gff文件中的attributes字段如何解析?
答:attributes字段采用键值对格式,如"ID=gene:AT1G01010;Name= protein_coding;biotype=protein_coding",可通过Python的re模块或专门的gff解析工具(如gffread)提取特定属性,提取基因ID可通过正则表达式"ID=([^;]+)"匹配。 -
问:ogs分析中如何区分直系同源和旁系同源基因?
答:直系同源基因是物种分化后由祖先基因垂直进化而来,通常保留相同功能;旁系同源基因则是基因复制后产生的同源基因,通过构建物种特异性系统发育树,可明确区分两类基因:若两个基因分别来自不同物种且位于不同进化分支,则为直系同源;若在同一物种内形成分支,则为旁系同源。